17 个常染色体STR 基因座在基诺族人群的遗传多态性研究
赵 凯,张韵梅,王伟涛,李光兴
(云南鉴识司法鉴定中心,云南 芒市 678400)
自1987 年首次用于刑事案件以来,对生物证据DNA 的分析彻底改变了法医调查技术。在这三十年中,DNA 分析方法的辨别能力、速度和灵敏度以及分型越来越具有挑战性的样品的能力取得了重大进展。通过建立罪犯和犯罪现场概况以及群体等位基因频率数据库,可以从犯罪现场样本中识别嫌疑人,并制定评估DNA 证据的统计框架。短串联重复序列(STR)作为目前人类身份个体识别最高效的DNA 分子标记,广泛地应用于法庭科学技术中,因STR 等位基因座在不同群体中存在比较明显频率分布差异,对不同民族人群中进行频率调查,建立基础数据库,有很重要的意义。
基诺族古称“攸乐”,在1979 年被确认为我国第56 个民族[1],是云南省特有的少数民族,主要聚居于云南省西双版纳傣族自治州景洪市基诺山基诺族民族乡,根据2010 年全国第六次人口普查,基诺族总人口为2.3 万余人。基诺族日常生活中使用基诺语,属汉藏语系藏缅语族彝语支,基诺族没有文字,有与其他彝语支民族相似的创世神话及葫芦图腾信仰。在汉文献中,直到清朝初期才有关于“攸乐”人的零星记载。
此调查为云南省基诺族人群的法医学个人识别和亲子鉴定以及群体遗传学研究提供基础数据。
1 材料与方法
1.1 样本
根据知情同意原则,收集云南省西双版纳傣族自治州景洪市基诺山基诺族民族乡331 例基诺族无关个体的颊粘膜拭子样本。
1.2 DNA 提取、扩增及检测
使用chelex-100 螯合树脂(伯乐生命医学产品(上海)有限公司)热裂解法提取拭子样本DNA,使用AGCU 17+1 试剂盒(无锡中德美联生物技术有限公司),扩增体系配制操同产品说明书,总反应体系 10 µL,在9700 型PCR 仪(美国Thermo Fisher Scientific 公司)上进行直接复合扩增,95 ℃2 min,94 ℃ 15 s、61 ℃ 40 s、65 ℃ 50 s、30 个循环,72 ℃ 10 min。取 1 µL 扩增产物与 0.5 µL 内标 LIZ500 和 9.5 µL 去离子甲酰胺混合,3130 基因分析仪(美国Thermo Fisher Scientific 公司)上进行全自动毛细管电泳,用 GeneMapper®ID-X 软件进行等位基因分型。选择F312(苏州阅微基因技术有限公司)为阳性质控品,纯化水为阴性质控品。
1.3 统计学处理
应用 Powerstates 软件[2]对STR 分型数据进行处理,计算获得17 个 STR 基因座的等位基因频率和法医学常用参数。使用Arlequin 3.5 软件[3]进行基因座间连锁不平衡检验(哈温平衡检验)。应用dispan 软件计算基诺族与其他10 个群体[4-13],利用MEGA 软件[14]基于DA distances构建邻接法进化树。
2 结果
2.1 等位基因频率分布及群体遗传学参数
本研究在331 名基诺族无关个体共观察到186 个等位基因和615 种基因型,等位基因频率分布在0.001 5~0.561 9(表1)。经过Bonferroni 矫正,基因型分布均符合哈温平衡(P> 0.002 9)。基诺族人群Ho 值分布在0.613 29~0.876 13,Penta E 和FGA 为高多态性基因座(PIC > 0.85),DP 值在0.770 5~0.968 9,累积个体识别率(CDP)达到0.999 999 999 999 999 999 999 9,PE 值 在0.307 1~0.747 0,三联体累积非父排除率(CPE)达到0.999 999 932,见表2。
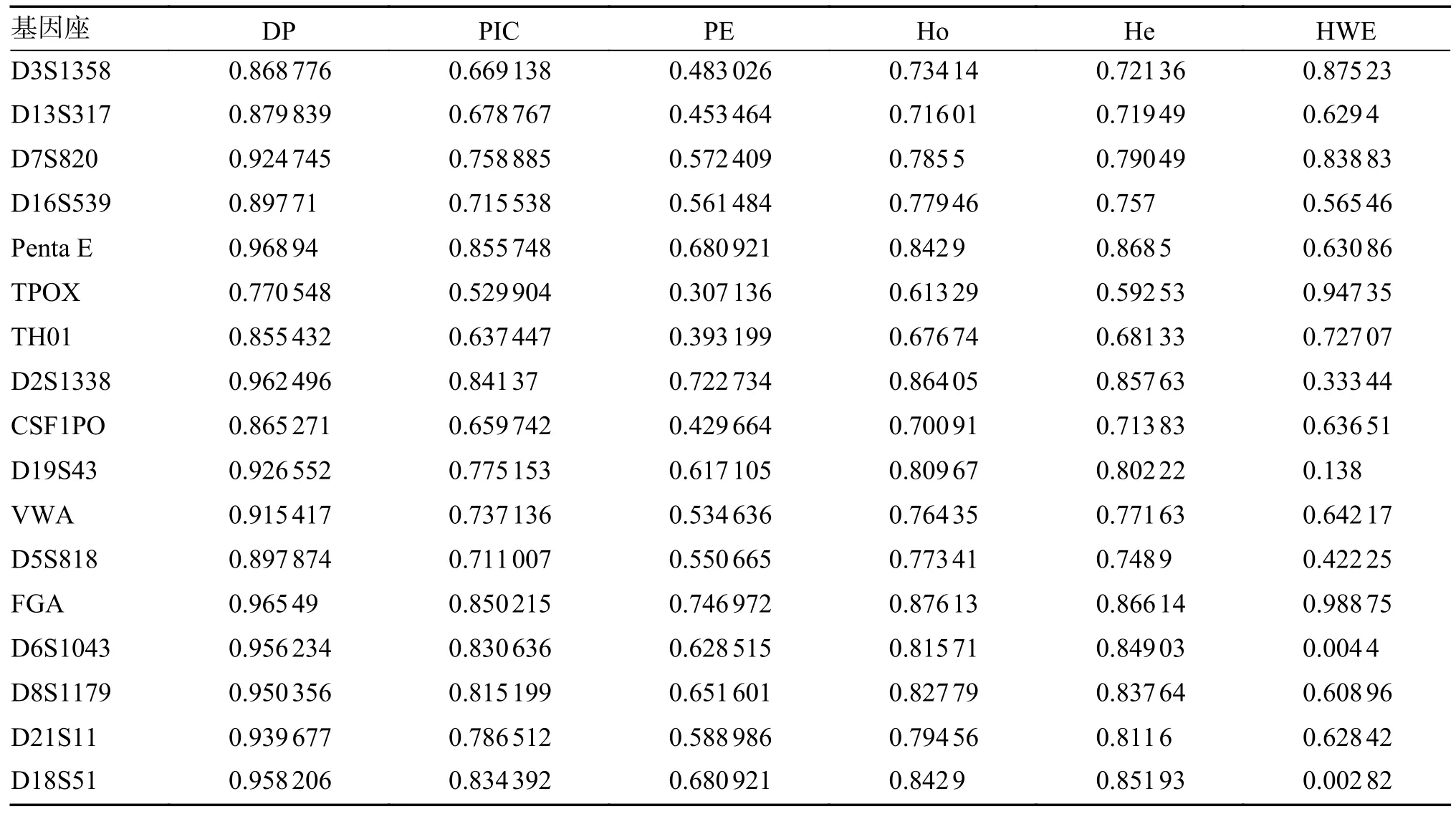
表2 基诺族人群17 个 STR 基因座法医学参数(n=331)Tab.2 Forensic parameters of 17 STR loci in the Jino people(n=331)
2.2 群体遗传结构分析
基诺族人群与白族、傣族、纳西族等10 个人群常染色体STR 基因座邻接法(Neighbor-Joining Algorithm)进化树结果见图1,遗传距离参数见表3,以云南南北不同地势、海拔为界分为两组,基诺族与聚居在南边的哈尼族和傣族聚类。
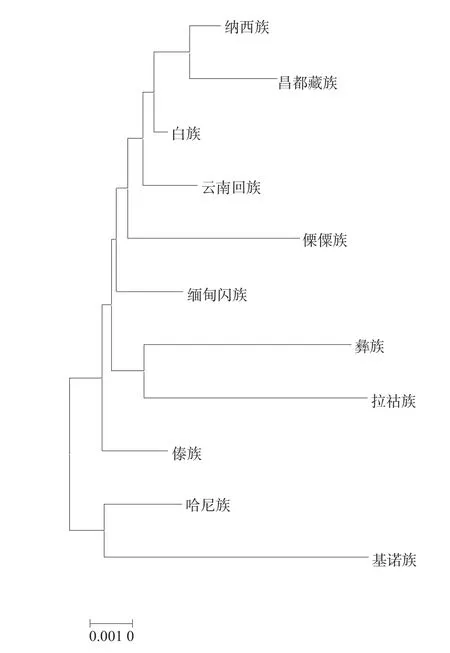
图1 基于DA distances 构建邻接法进化树。Fig.1 Neighbor-Joining tree based on DA distances.

表3 基诺族人群与白族、傣族、纳西族等10 个人群 Standard genetic distances(左下)和Standard error(右上)Tab.3 Standard genetic distances(bottom left)and Standard error(top right)of Jino people and 10 other groups
3 讨论
在法医DNA 分析中,随机匹配概率(RMP)是普通人群中随机的、无关的人表现出与嫌疑人匹配的DNA 图谱的概率,DNA 图谱越罕见,已知和质疑的证据来自同一个人的几率就越大。基于毛细管电泳技术开发的STR 基因座检测试剂盒通常以CODIS 位点为核心,增加性别、Y-STR 或SNP 位点的方式进行设计。CODIS 位点覆盖了人基因组不同染色体的STR 基因座[15],且包含有序列复杂度较高的D8S1179、FGA、D21S11 基因座,在法医物证学的实践中,发现在不同的地区、人群中STR 基因座的识别效能存在比较大的差异,如TPOX 和TH01 基因座,在我国人群的识别效能都不算高,因此,对于不同群体进行基础的人群频率调查,有利于评估试剂盒的实用性。以本研究结果为例,按 DP≥ 0.9、H ≥ 0.7、PIC ≥0.7 的 STR 基因座属高度多态性基因座的标准来衡量,基诺族17 个常染色体STR 基因座中,TPOX、TH01 基因座多态性和识别能力最低,D3S1358、D13S317、D16S539、CSF1PO、D5S818均有参数显示多态性不佳。
所有基因座的基因型分布均符合哈温平衡,说明采样符合随机性要求,同时各基因座间相互独立。根据乘积原则,AGCU 17+1 试剂盒在基诺族人群中具有较好的个体识别和亲权鉴定的系统效能(CDP > 0.999 999 999、CPE > 0.999 999),考虑到部分基因座多态性不佳的情况,可以适当增加试剂盒检测的基因座个数,从而提高试剂盒的识别能力。CODIS 核心STR 数据库于2015 年进行了拓展,核心CODIS 基因座变为19 个[15],增加了7 个基因座(D2S1338、D19S433、D1S1656、D12S391、D2S441、D10S1248 以及 DYS391),剔除了 TPOX 基因座。根据基诺族17 个常染色体STR 基因座人群频率调查结果,TPOX、TH01 基因座多态性差,虽然17 个基因座联合使用具有较高的识别能力,建议增多等位基因座检测或选择不含TPOX 和TH01 基因座试剂盒进行该人群法医学个人识别和亲权鉴定,尤其是特殊亲权鉴定,如祖孙鉴定、同胞鉴定等情况[16]。在法医学实践中,应该以本国人群的STR 基因座数据,筛选合适的高识别度的基因座,形成核心基因座+高特异性基因座联检试剂盒。
本研究所调查的基诺族群体属于云南人口较少的少数民族,主要聚居于西双版纳基诺乡。从遗传距离来看,基诺族与同属于彝语支的哈尼族汇聚在一起,虽然基诺族与傣族在聚居地重叠,但是在遗传距离数据看,用语系进行结构分类更具有接近度,提示基诺族由北方迁徙而来的观点有一点的合理性。

